前言
分子定向進化是利用現代分子生物學方法,人為模擬自然進化機制,人工合成大量的突變同源基因文庫。采用靈敏的定向篩選策略,創造出自然界不存在的或某些特性有顯著改變的突變蛋白質或其他生物分子。
01
精準突變文庫類型
精準突變文庫,融合了基因合成、基因突變和定向進化研究的精華。它通過改變蛋白質的特定位點或DNA的調控區域,來研究結構和功能之間的關系。突變文庫的主要類型包括:
丙氨酸掃描文庫
Alanine Scan Library
實現全面突變覆蓋的高級策略
利用丙氨酸體積小同時對蛋白質結構影響較小的特性,科學家通過丙氨酸系統地取代其他19個氨基酸殘基的每一個,構建了丙氨酸掃描文庫。這種創新方法通過探索單個氨基酸殘基在蛋白質功能、活性位點和穩定性中的作用,解開了蛋白質結構和功能的秘密。

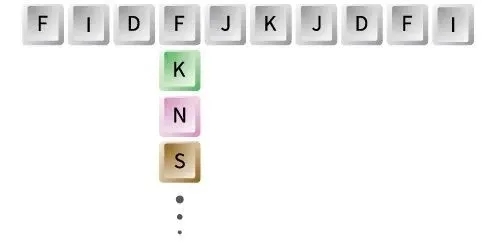
定點飽和突變文庫
Site-Saturation Mutagenesis Library
實現單點氨基酸的精確突變
將蛋白序列限定區域內的氨基酸位點突變成另外的19種氨基酸,構成定點飽和突變文庫。一次只突變一個氨基酸位點,每條序列和模板相比只存在一個氨基酸位點突變。這可以大幅降低引物合成成本,對于突變位點多的高庫容文庫極具優勢。
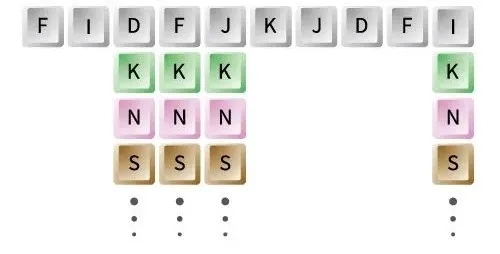
組合突變文庫
Combinatorial Mutagenesis Library
實現多點多種氨基酸的精確突變
將蛋白序列的限定區域內連續的幾個氨基酸位點同時突變成另外的19種氨基酸,構成組合突變文庫。同時突變多個氨基酸位點,每條序列和模板相比存在多個氨基酸位點突變。為研究復雜蛋白結構與功能的關系以及進行蛋白工程、抗體研究提供了強大的實驗工具。
02
精準突變文庫構建流程
精確突變庫旨在為研究人員提供高度精確的基因突變資源。根據設計目的不同,體外合成的精準突變文庫可以更精確、更隨意地控制所研究序列的多樣性,有助于深入探究基因功能和調控機制。基于芯片構建精準突變文庫的流程如下:
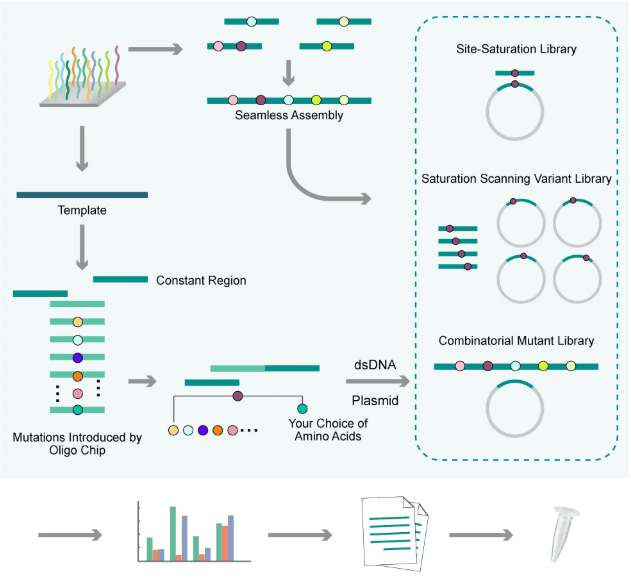
-
通過芯片引物引入突變。 -
對樣品中的DNA進行大量PCR擴增。 -
將dsDNA片段無縫組裝到質粒上。 -
對得到的突變文庫進行測序驗證及數據分析。
03
精準突變文庫的應用領域
定向進化研究:構建突變文庫有助于探索基因的功能和調控機制,推動基礎科學研究的進展。
酶工程改造:用于改良酶的催化性能和微生物的代謝途徑,為酶工程提供高效、精準的生物工具。
生物醫藥領域:用于篩選藥物靶點的關鍵功能區域,發現與疾病相關的新藥物靶點,促進新藥開發和研究。
農業領域:有助于篩選具有改良性狀的抗體、配體及受體,提高作物產量、抗病性和適應性。
食品領域:針對食品中存在的特定蛋白質進行定向進化,改善其功能性和營養價值,有助于提升食品的品質和營養水平。
Synbio Technology
合成生物學賦能技術平臺
泓迅生物依托領先設計和先進制造成功交付了數百個高質量、定制庫化的精準突變文庫。我們根據您的需求,精心設計并合成各種DNA精準突變文庫,為您提供定制化基因突變文庫解決方案。
服務優勢
序列控制精準
合成效率高
高度定制化
高性價比方案
泓迅案例
NNK文庫是一種經典的簡并突變文庫,所使用的 NNK簡并引物包含了32(4x4x2)種密碼子組合(N= A/C/G/T, K= G/T),覆蓋了所有20種氨基酸,可以將任意位點的氨基酸進行飽和突變。
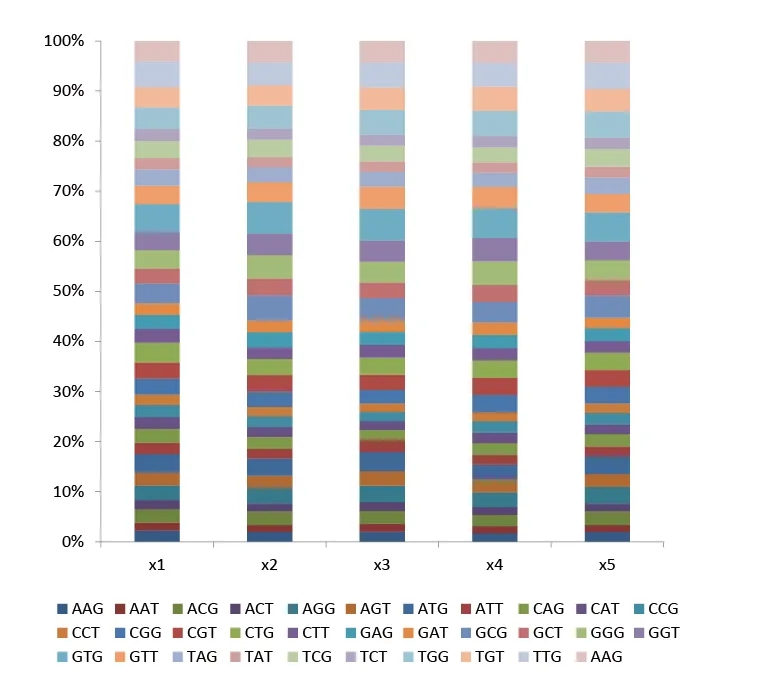
NNK文庫,5個NNK位點所包含的每種密碼子的比例
References
[1] Wang Y, Xue P, Cao M, Yu T, Lane ST, Zhao H. Directed Evolution: Methodologies and Applications. Chem Rev. 2021 Oct 27;121(20):12384-12444.
[2] Yu Q, Li Y, Wu B, Hu W, He M, Hu G. Novel mutagenesis and screening technologies for food microorganisms: advances and prospects. Appl Microbiol Biotechnol. 2020 Feb;104(4):1517-1531.
[3] Wang TW, Zhu H, Ma XY, Zhang T, Ma YS, Wei DZ. Mutant library construction in directed molecular evolution: casting a wider net. Mol Biotechnol. 2006 Sep;34(1):55-68.
[4] Williams G J, Domann S, Nelson A, et al. Modifying the stereochemistry of an enzyme-catalyzed reaction by directed evolution[J]. Proceedings of the National Academy of Sciences, 2003, 100(6): 3143-3148.
 Syno?C 引物合成
Syno?C 引物合成 RNA合成
RNA合成 mRNA合成
mRNA合成 Syno?GS 基因合成
Syno?GS 基因合成 載體構建
載體構建 高通量及DNA文庫構建
高通量及DNA文庫構建 CRISPR基因編輯平臺
CRISPR基因編輯平臺 病毒包裝
病毒包裝 基因測序及分析
基因測序及分析 重組蛋白表達平臺
重組蛋白表達平臺 抗體工程平臺
抗體工程平臺 多肽服務
多肽服務 生物信息學分析與設計
生物信息學分析與設計 CRISPR文庫
CRISPR文庫 ProXpress蛋白快速檢測
ProXpress蛋白快速檢測 CRISPR 質粒
CRISPR 質粒





















